ggplot画热图 合并细胞组合细胞 单细胞基因整体表达量 合并多个细胞整体表达量条形热图 合并热图
多个 合并 组合 整体 基因 表达 单细胞 细胞
2023-09-14 09:09:48 时间
input
library(reshape2)
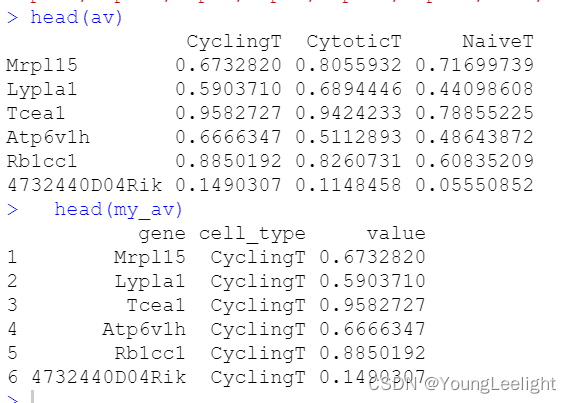
my_av=melt(av,value.name = "value")
head(my_av)
colnames(my_av)=c('gene','cell_type','value')
ggplot(my_av[round(runif(100,1,nrow(my_av))),],
aes(x=gene,y=value,fill = cell_type),color=cell_type)+
geom_boxplot()
mydata=my_av[round(runif(100,1,nrow(my_av))),]
head(mydata)
p1=ggplot(mydata,aes(x=cell_type,y=gene,fill=value))
p2 <- p1+geom_raster()+scale_fill_gradient2(low="#003366", high="#990033", mid="white")
p2
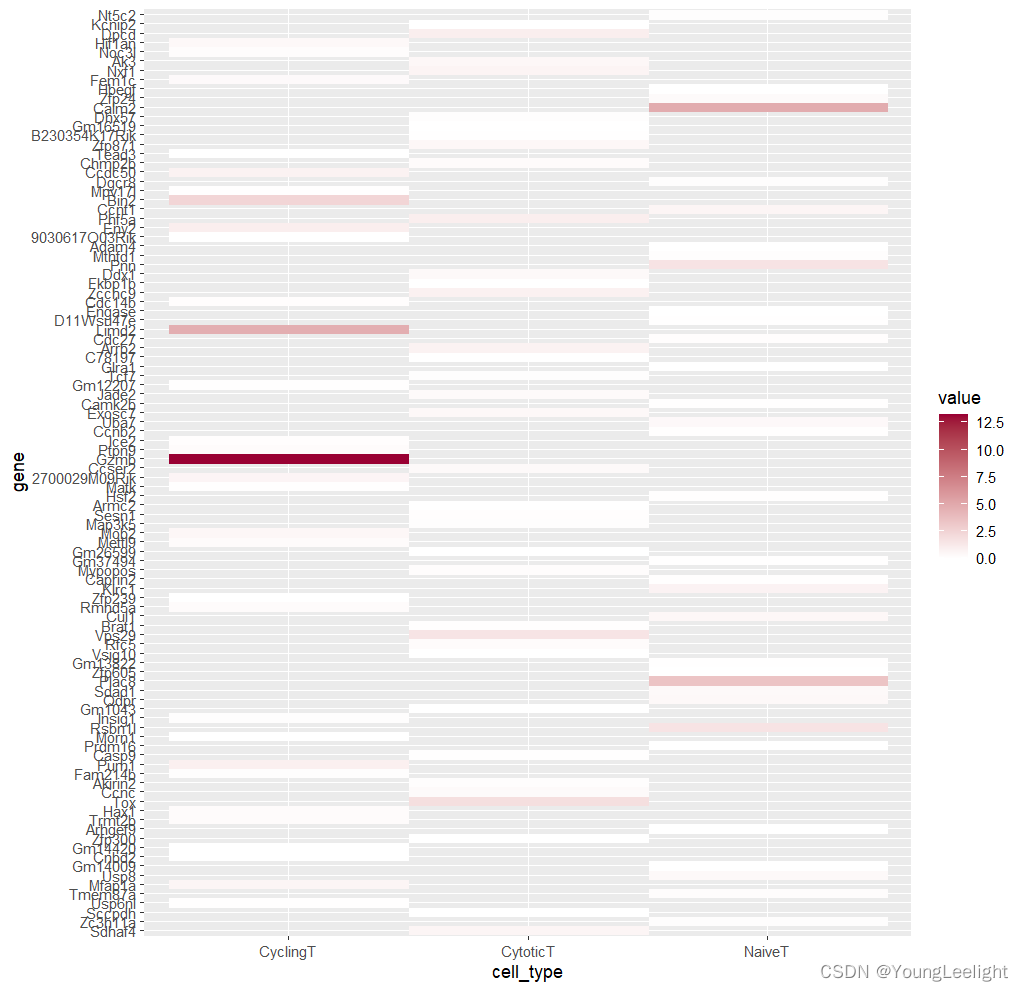
pheatmap::pheatmap(av[round(runif(100,1,nrow(av))),])
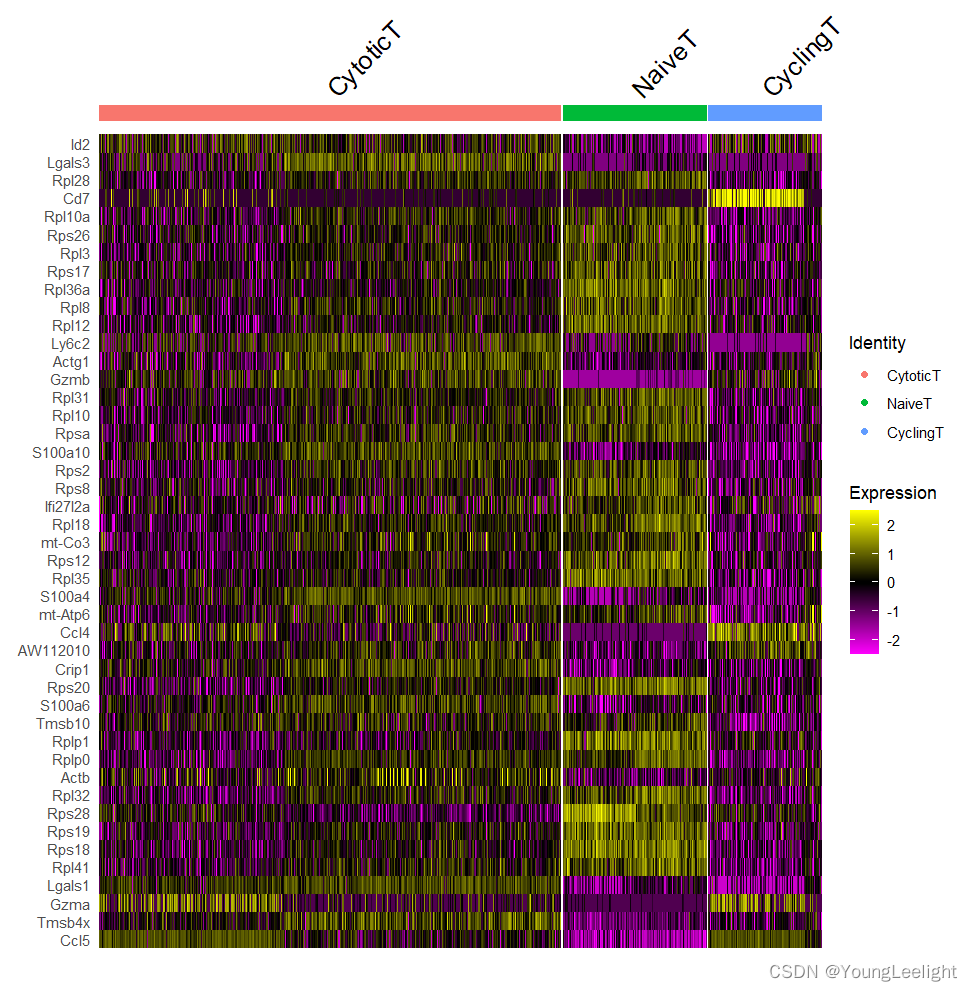
DoHeatmap(sce.all,features = cg)
``go
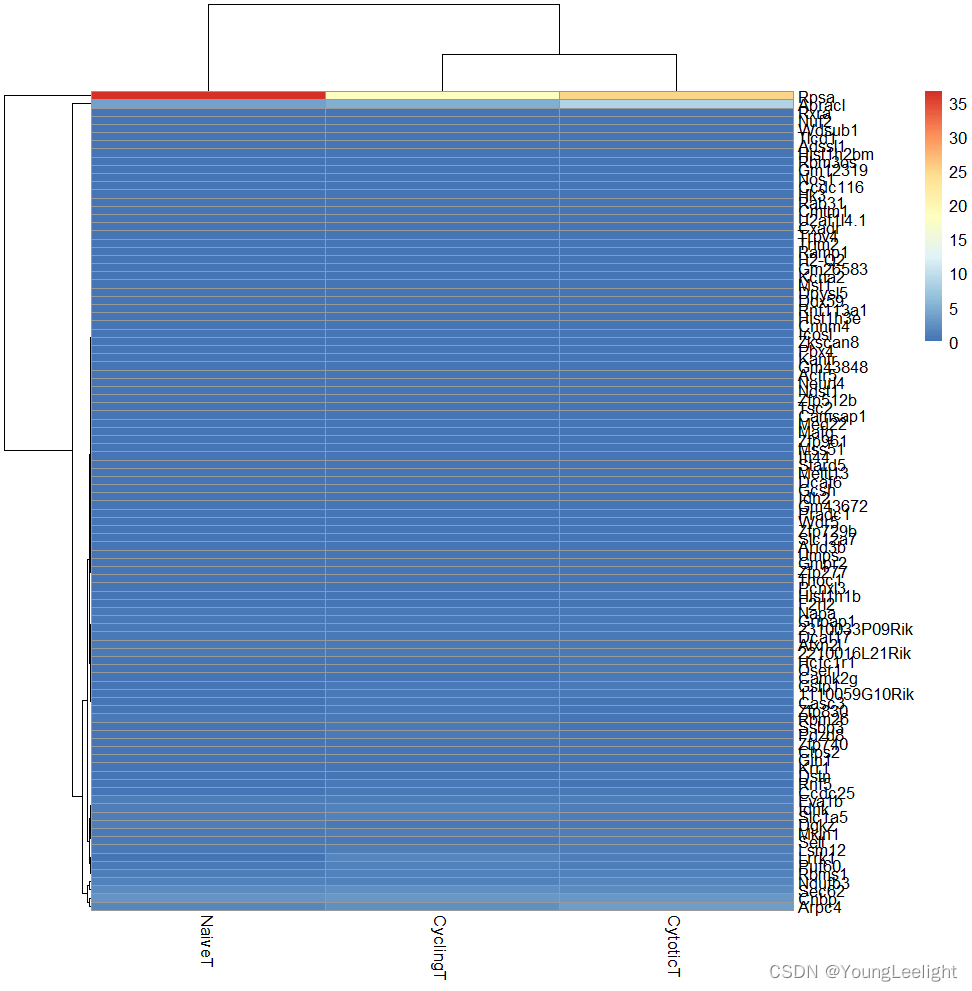
整体表达量,绘制细胞类型之间的平均值相关性热图 -------------------------------------------------------
先展示一下Marker基因在细胞类型之间的表达情况
dev.off()
FeaturePlot(sce.all,‘Ccl5’)+DimPlot(sce.all,label = T,repel = T)
ggsave(‘Lum-and-umap-celltype.pdf’,width = 5,height = 8)
av <-AverageExpression(sce.all,
group.by = “celltype”,
assays = “RNA”)
av=av[[1]]
head(av)
write.csv(av,file = ‘AverageExpression-celltype.csv’)
cg=names(tail(sort(apply(av, 1, sd)),1000))
pheatmap::pheatmap(cor(av[cg,]),display_numbers = T)
pheatmap::pheatmap(cor(av[cg,]),display_numbers = T,
file = ‘AverageExpression-celltype.pdf’)
dev.off()
相关文章
- 下载网络直播,多个ts文件下载与合并
- Python提取多个pdf首页合并输出
- 多个单细胞样本数据的循环读取
- linux下gcc编译多个源文件、gdb的使用方法详解程序员
- 性约束MySQL实现多个字段唯一性约束(mysql多个字段唯一)
- 使用Oracle合并多个字段(oracle字段合并)
- 的判断Linux下如何进行多个条件判断(linuxif多个条件)
- Linux合并多个文件的简单方法(linux多个文件合并)
- 如何使用 Apache Web 服务器配置多个站点
- SQLServer 并集:如何合并多个表的数据?(sqlserver并集)
- MySQL如何实现两个表多个列的合并(mysql 两表多列合并)
- Oracle临时表合并把多个短期存活存储使用同一片段(oracle临时表合并)
- MySQL多个结果合并技巧如何合并不同的查询结果(mysql 不同结果合并)
- MySQL 多个字段合并简单实用的方法(mysql 不同字段合并)
- 语句利用Oracle构建复杂条件判断多个If语句讲解(oracle使用多个if)
- MySQL多个字段取并集,轻松实现数据筛选和合并(mysql不同字段取并集)
- PHP根据传入参数合并多个JS和CSS文件的简单实现
- phpswitch语句多个值匹配同一代码块应用示例
- JavaScript及jquey实现多个数组的合并操作

