Nature:哈佛&牛津开发最新AI模型,已预测3600万个致命基因突变
本文经AI新媒体量子位(公众号ID:QbitAI)授权转载,转载请联系出处。
直接从基因层面预测疾病,这一直是近现代医学研究的主要方向之一。
然而,全体人类的基因变异体数量远超现有的探测技术,甚至仅仅是不同个体的蛋白质区编码也会展现出巨大的差异性。
因此,超过98%的基因变异给人体带来的影响依旧是未知且无法预测的。
但最近,来自哈佛医学院和牛津大学的科学家合作开发了一种AI模型,成功预测了3219个疾病基因中超过3600万个变体的致病性,并将超过25万个未知变体进行了归类。

这项研究现已登上Nature。
“从进化中预测致病性”
其实,现在临床上已有用于预测基因变异影响的模型。
但这些模型往往是在经过标注的临床数据集上进行有监督学习,一旦进入现实场景,标签偏差、标签稀疏以及噪音就会造成其准确率的下降,并不能作为基因变异体分类的可靠依据。
而这次的研究团队提出了一个叫做EVE(Evolutionary model of Variant Effect)的模型。
这是一个仅根据进化序列训练的无监督生成模型。
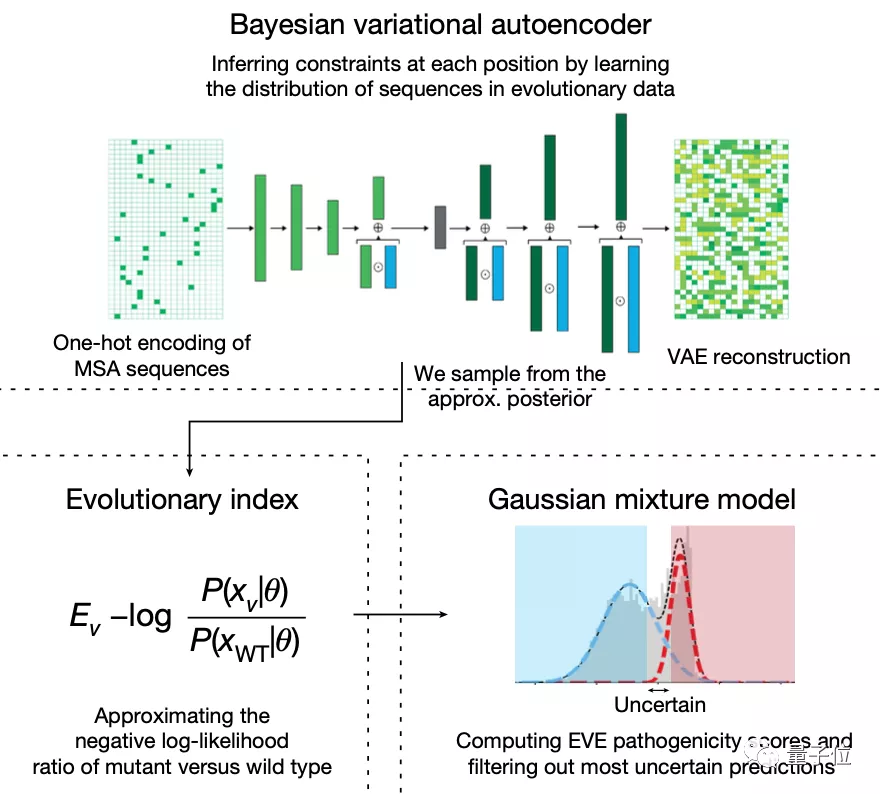
模型预测变异基因的致病性主要分为两步:
第一步,使用变型自动编码器VAE来学习蛋白质的氨基酸序列分布。
学习了多个领域的复杂高维分布之后,模型就捕捉到了进化过程中的自然序列约束,包括各种位置之间的复杂依赖关系。
再从得到的近似后验分布(Approximate Posterior Distribution)中取样,评估每个单一氨基酸变体相对于野生型的相对可能性。
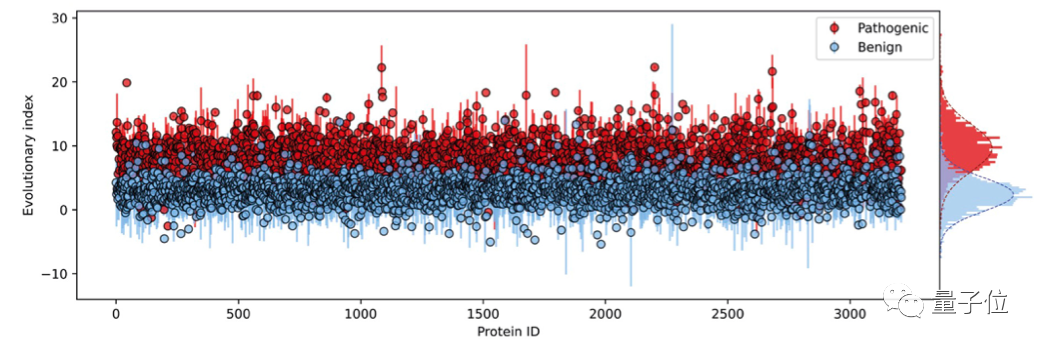
这种相对可能性被称为“进化指数”,与临床标签进行比较后发现,区分致病性和良性标签的数值在不同的蛋白质中是一致的,这说明无监督的方法能够有效推断致病性。
第二步,在所有单一氨基酸变体的进化指数分布上拟合了一个双组分(two-component)的全局-局部高斯混合模型。
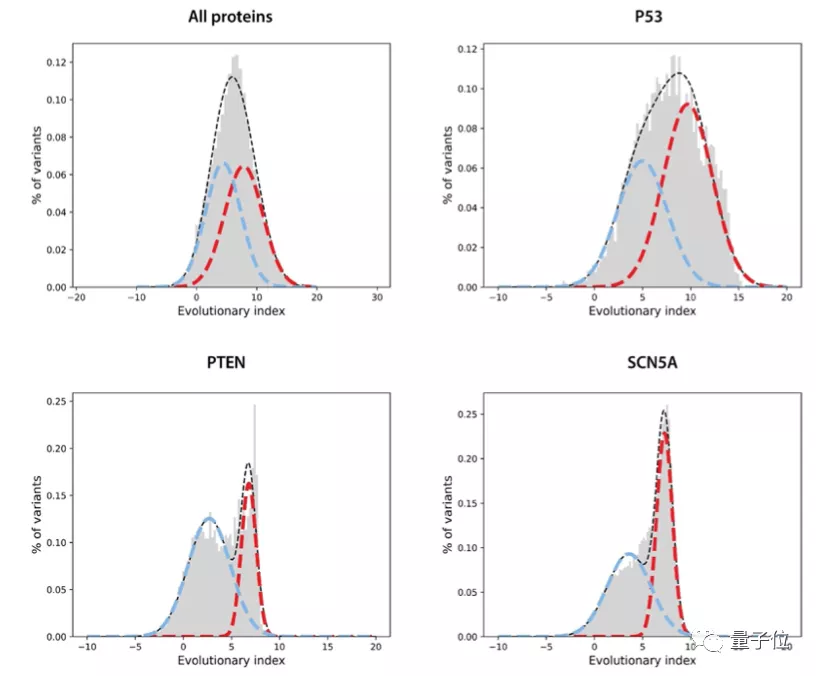
这一步的输出是在区间[0,1]内定义的连续致病性值,0代表良性,1代表致病性。
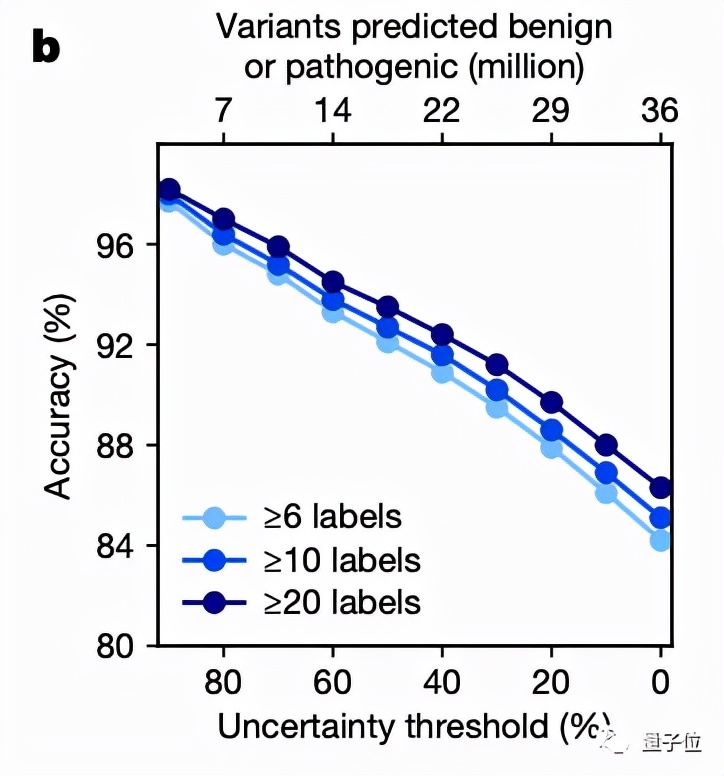
然后将EVE模型运用于ClinVar数据库中的3219个人类基因上,得到的结果图中的平均曲线面积(AUC)为0.91,说明EVE模型对绝大多数的基因变异都能做到具有临床意义的预测:
优于已知模型,与实验预测效果一致
研究团队也将EVE模型与已知的模型进行了对比,可以看到,在预先确定已知的已标注临床数据的预测上,其效果优于同类计算模型:
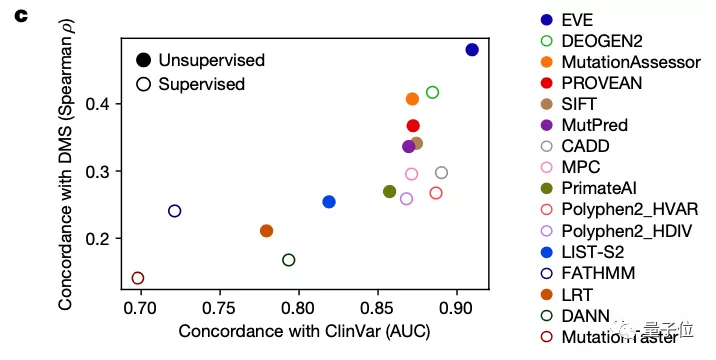
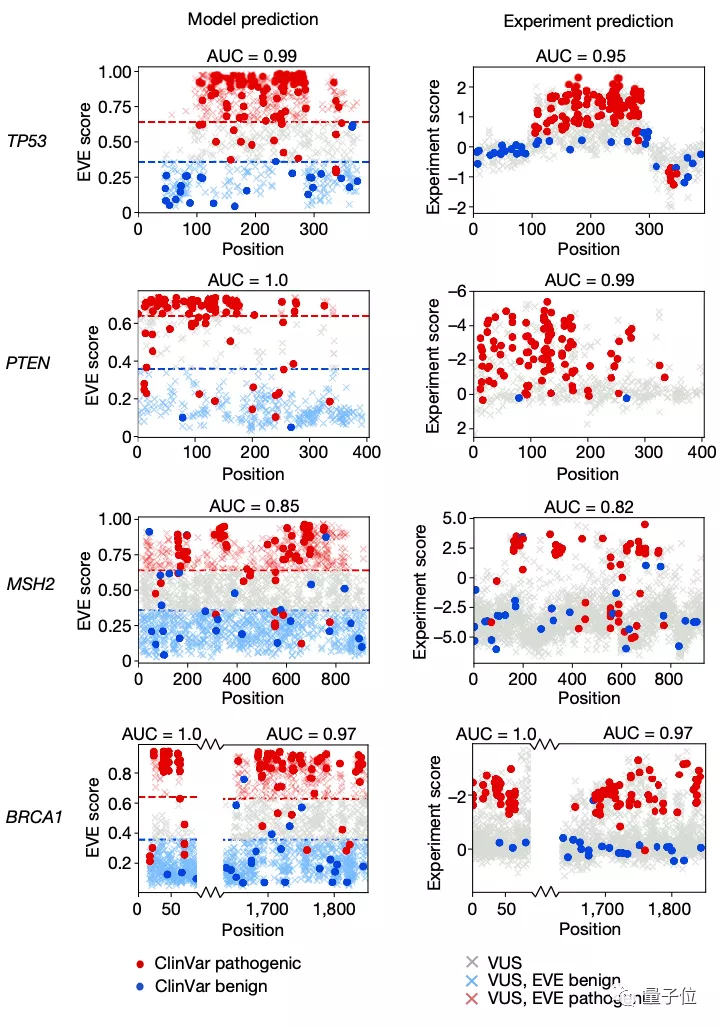
那么这样一个AI计算模型与用于预测致病性的经典方法——深度突变扫描实验(Deep Mutational Scan Experiment)相比效果又如何呢?
对比实验后可以看到,EVE模型在临床预测方面的总体表现与经典方法效果基本一致:
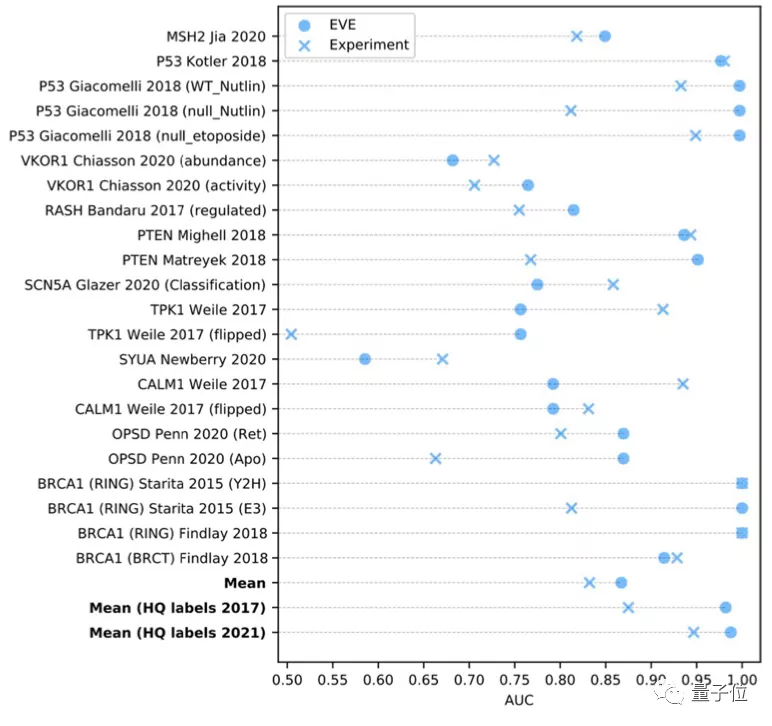
而当从ClinVar数据库中选择一组数量规模更大,但高质量标注较小的数据时,EVE模型的表现甚至更好:
哈佛&牛津合作出品
这篇论文有三位共同一作,其中Jonathan Frazer和Mafalda Dias都来自哈佛大学的系统生物学,他们同时也是Marks Group实验室中的一员。


而Pascal Notin则是来自牛津大学的计算机科学专业的博士生,主要研究领域包括贝叶斯深度学习、生成模型、因果推理和计算生物学的交叉领域。

论文链接:
https://www.nature.com/articles/s41586-021-04043-8
相关文章
- 金融服务领域的大数据:即时分析
- 影响大数据、机器学习和人工智能未来发展的8个因素
- 从0开始构建一个属于你自己的PHP框架
- 如何将Hadoop集成到工作流程中?这6个优秀实践必看
- SEO公司使用大数据优化其模型的5种方法
- 关于Web Workers你需要了解的七件事
- 深入理解HTTPS原理、过程与实践
- 增强分析:数据和分析的未来
- PHP协程实现过程详解
- AI专家:大数据知识图谱——实战经验总结
- 关于PHP的错误机制总结
- 利用数据分析量化协同过滤算法的两大常见难题
- 怎么做大数据工作流调度系统?大厂架构师一语点破!
- 2019大数据处理必备的十大工具,从Linux到架构师必修
- OpenCV中的KMeans算法介绍与应用
- 教大家如果搭建一套phpstorm+wamp+xdebug调试PHP的环境
- CentOS下三种PHP拓展安装方法
- Go语言HTTP Server源码分析
- Go语言HTTP Server源码分析
- 2017年4月编程语言排行榜:Hack首次进入前五十



